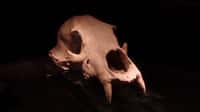
C'est une découverte extraordinaire : des fragments d'ADN datant d'il y a deux millions d'années, qui battent l'ancien record de près d'un million d'années ! Trouvés dans une formation géologique au nord du Groenland, ces échantillons ont permis aux scientifiques de reconstituer l'écosystème qu'abritait la région à l'époque : au lieu du désert polaire actuel, le Groenland abritait une grande forêt regorgeant d'êtres vivants !
au sommaire
Jusqu'à aujourd'hui, le plus vieil échantillon d'ADNADN retrouvé et séquencé correspondait à celui d'un mammouth, et datait d'il y a environ 1,2 million d'années. Mais de nouveaux échantillons battent ce record de près d'un million d'années, découverts au Groenland et âgés de deux millions d'années ! Ces fragments d'ADN microscopiques ont été découverts dans une formation géologique au nord du Groenland, appelée Kap Kobenhavn. On trouve dans ce désert polaire différents sédiments datant de la dernière période glaciaire, qui a débuté il y a 110 000 ans et s'est achevée il y a 10 000 ans. Et sur ces sédiments qui s'accumulent sur près de 100 mètres d'épaisseur, des chercheurs ont prélevé 41 échantillons d'ADN environnemental cachés dans l'argile et le quartzquartz ! Ils correspondent à différents êtres vivants, allant du lièvre au renne, en passant par des rongeursrongeurs, des oiesoies, ou encore des essences d'arbresarbres comme les bouleaux !

Une conservation exceptionnelle de l'ADN, car « ces anciens échantillons ont été retrouvés profondément enfouis dans des sédiments qui s'étaient accumulés pendant plus de 20 000 ans. Le sédiment a été préservé dans la glace ou le pergélisolpergélisol et, surtout, n'a pas été dérangé par l'homme pendant deux millions d'années », explique le premier auteur d'une étude publiée dans la revue Nature Kurt H. Kjær, paléontologuepaléontologue à l'université de Copenhague. En effet, « l'ADN survit généralement mieux dans des conditions froides et sèches telles que celles qui ont prévalu pendant la majeure partie de la période depuis que le matériaumatériau a été déposé à Kap Kobenhavn », a ajouté le généticiengénéticien Eske Willerslev, coauteur de l'étude.
De quoi donner de l'espoir pour de futures trouvailles, là où le climatclimat n'était pas que glaciaire, et peut-être remonter à l'origine de certaines espèces ! « Maintenant que nous avons réussi à extraire l'ADN ancien de l'argile et du quartz, il est possible que l'argile ait conservé l'ADN ancien dans des environnements chauds et humides sur des sites trouvés en Afrique, s'enthousiasme Eske Willerslev. Si nous pouvons commencer à explorer l'ADN ancien des grains d'argile d'Afrique, nous pourrons peut-être recueillir des informations révolutionnaires sur l'origine de nombreuses espècesespèces différentes - peut-être même de nouvelles connaissances sur les premiers humains et leurs ancêtres. Les possibilités sont infinies. »

Il y a deux millions d'années, le Groenland abritait un écosystème prospère
À partir de ces découvertes, les scientifiques ont tenté de reconstituer l'écosystème qui devait se trouver là. Car deux millions d'années auparavant, au début du PléistocènePléistocène, le climat, comme l'expliquent les auteurs, était bien plus chaud qu'aujourd'hui. « Les enregistrements paléoclimatiques montrent une forte amplification polaire avec des températures annuellesannuelles moyennes de 11 à 19 °C au-dessus des valeurs contemporaines », décrit l'étude. Les glaciations alternaient avec des périodes bien plus chaudes, ressemblant à ce qui pourrait bien nous attendre à l'avenir.
Sur les 41 fragments d'ADN, ils ont obtenu 65 séquençagesséquençages différents. Ils ont établi, grâce aux différents sédiments et fragments d'ADN retrouvés, que l'écosystèmeécosystème était constitué de nombreux arbres différents, regroupés en une forêt boréale : bouleaux, peupliers, thuyas, et de nombreux arbustes. Au total, « cinq fois plus de genres de plantes que les études précédentes », cite l'étude. Parmi eux, « beaucoup n'avaient pas été détectés auparavant sur le site à partir d'enregistrements de macrofossiles et de pollenpollen », expliquent les chercheurs. En hiverhiver, la température moyenne avoisinait les -17 °C, et l'été les 10 °C, si bien que la calotte glaciairecalotte glaciaire variait au cours de l'année.
Les animaux qui peuplaient le nord du Groenland se sont aussi révélés bien plus nombreux, avec « la détection à la fois de Rangifer (renne et cariboucaribou) et de Mammut (mastodon) », remettant à nouveau en question les études précédentes. L'équipe compte publier prochainement une nouvelle étude qui reconstituera entièrement cet ancien écosystème.

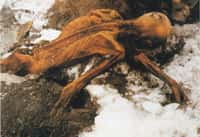
Cet ADN de mammouth est le plus vieux jamais séquencé
Article de Céline DeluzarcheCéline Deluzarche publié le 27/02/2021
Record doublé ! Des chercheurs ont séquencé un ADN vieux de 1,2 million d'années issu d'un mammouth congelé de Sibérie. Une découverte qui nous questionne sur la limite de conservation de l'ADN et fait ressurgir les fantasmes de Jurassic Park.
De l'ADN vieux de 1,2 million d'années a été séquencé par une équipe de chercheurs, constituant un nouveau record et repoussant encore un peu plus les limites du séquençage. L'ADN provient de trois mammouths retrouvés dans les années 1970 dans le pergélisol sibérien, et âgés respectivement de 1,65 million d'années, 1,34 million d'années et 870.000 ans, selon la datation géologique de la roche dans laquelle ils ont été trouvés (l'âge plus probable du plus ancien étant plutôt de 1,2 million d'années).
“Plus vous avez de pièces de puzzle, plus il est difficile de reconstruire l’ensemble”
Les chercheurs ont prélevé de minuscules échantillons de molairemolaire de chaque mammouth et ont tenté d'en extraire l'ADN. Une gageure, car au fil du temps, l'ADN se dégrade en des milliards de courts fragments. « Plus vous avez de pièces de puzzle, plus il est difficile de reconstruire l'ensemble », atteste dans le magazine Science Tom van der Valk, généticien à l'université d'Uppsala et principal auteur de l'étude parue dans la revue Nature. Pour reconstituer « l'image » du puzzle, les chercheurs ont pris comme référence des génomes d'éléphants et de mammouths plus jeunes déjà séquencés.

Deux espèces de mammouth ayant divergé il y a 2 millions d’années
L'ADN accumule les mutations au fil du temps sur un rythme assez constant. En comptant les mutations, il est donc possible de déterminer le temps entre deux évolutions comme, par exemple, le moment où une espèce se scinde en deux. C'est grâce à cette méthode que les chercheurs ont pu constater que les molaires proviennent de deux espèces de mammouths différentes. La première, le mammouth des steppessteppes, est bien connue : ses descendants sont les mammouths laineux. L'autre, la plus ancienne, provient d'un mammouth encore inconnu jusqu'ici, qui vivait en Sibérie et aurait divergé des autres espèces il y a environ 2 millions d'années. Une surprise pour les paléontologues, qui pensaient jusqu'ici qu'une seule espèce de mammouths avait occupé la Sibérie à cette époque.

Séquençage ADN : jusqu’où peut-on remonter dans le temps ?
« Cette étude repousse assez sensiblement les limites du séquençage ADN », relève Beth Shapiro, une des coauteurs et biologiste à l'Université de Californie à Santa Cruz. Le précédent record remontait à 2013 avec le séquençage d’un ADN de cheval dont l'ADN avait entre 560.000 et 780.000 ans. Le matériel génétiquematériel génétique est relativement fragile et se décompose rapidement dans la plupart des environnements. En théorie, une moléculemolécule d'ADN se désagrège de moitié tous les 521 ans, de telle sorte qu'au bout de 1,5 million d'années, il n'en reste pratiquement plus.
Mais, dans ces conditions particulières, comme dans le pergélisol où l'ADN est à l'abri de l'humidité et du rayonnement solairerayonnement solaire, il peut persister beaucoup plus longtemps. Selon Tom van der Valk, il serait donc possible de séquencer de l'ADN aussi vieux que le pergélisol lui-même, c'est-à-dire 2,6 millions d'années. Mais même de bonnes conditions de conservation ne sont pas une garantie de succès. En 2019, Love Dalén, l'un des coauteurs de la nouvelle étude, avait tenté d’extraire de l’ADN de dents de rhinocéros datant de 1,7 million d'années, mais n'avait réussi à récupérer que des protéinesprotéines, qui ne contiennent qu'une petite partie du code génétiquecode génétique.
Ressusciter un mammouth : un rêve encore bien lointain
On est donc encore bien loin de Jurassic Park, les derniers dinosauresdinosaures datant de 66 millions d'années. Quant à faire revivre le mammouth laineux, les obstacles demeurent là aussi épineux. La tentative la plus sérieuse est celle du généticien George Church, de l'université de Harvard, qui compte implanterimplanter des gènesgènes de mammouth dans un embryonembryon d'éléphant d'Asie. Une sorte d'hybridehybride qui donnerait lieu à une nouvelle espèce, mais qui n'est aucunement une résurrection du mammouth laineux tel qu’il vivait il y a 4.000 ans.