au sommaire
Si les acides nucléiques (ADN et ARN) demeurent indispensables à tout être vivant, ils ne jouent que le rôle de support de l'information génétique. Celle-ci est ensuite interprétée par des organites appelés ribosomes, qui vont traduire le message et synthétiser des protéines, des moléculesmolécules indispensables qui participent à l'essentiel de l'activité cellulaire.
Le système naturel est extrêmement performant, un ribosome pouvant assembler une vingtaine d'acides aminésacides aminés (les constituants de base d'une protéineprotéine) chaque seconde. De quoi inspirer les chimistes du monde entier, qui y voient un moyen de produire massivement des composés particuliers.
Des chercheurs de l'université de Manchester (Royaume-Uni) ont suivi cette piste et annoncent dans la revue Science avoir développé un nanorobot capable d'additionner des acides aminés pour former une courte séquence protéique.
Un nanorobot qui empile les acides aminés
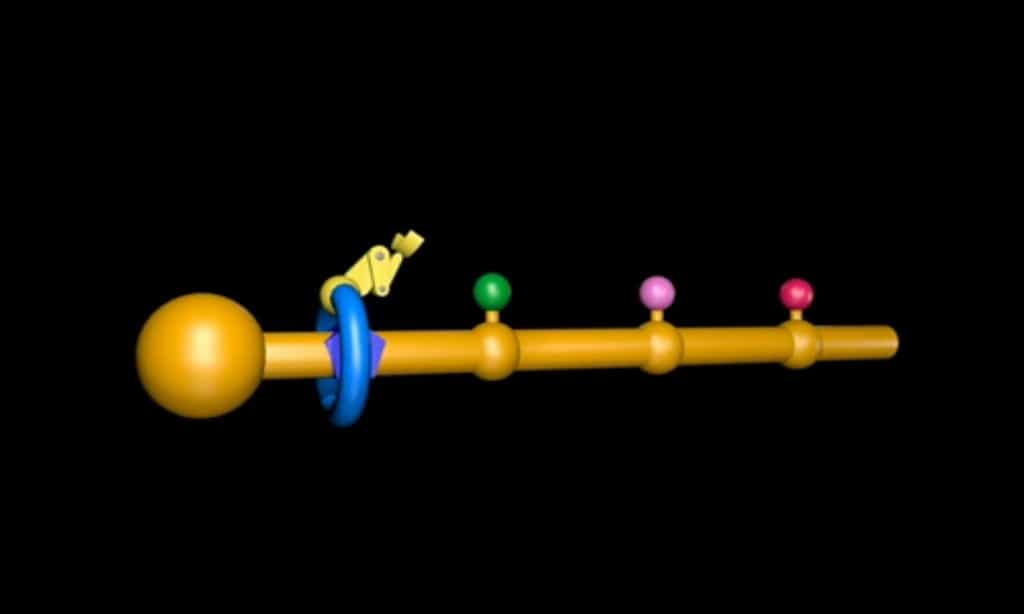
Leur machine est bien plus simple que le ribosome et ne mesure qu'un dixième de sa taille. Il repose sur un rotaxanerotaxane, littéralement une roue autour d'un axe. Comme le montre le schéma ci-dessous, il s'agit d'une molécule circulaire placée autour d'une molécule axialeaxiale, le long de laquelle elle peut progresser.
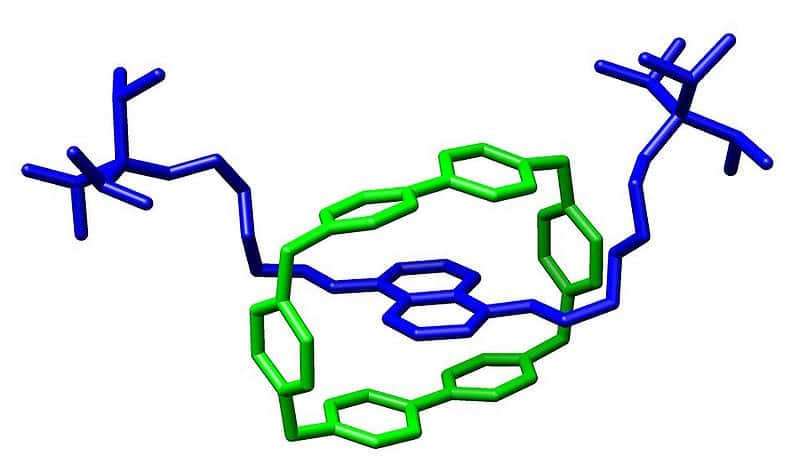
Un exemple de rotaxane. Un macrocycle (en vert) est traversé par une molécule longiligne (en bleu). © M stone, Wikipédia, cc by sa 3.0
Ce nanorobot se forme grâce à l'activité d'ionsions cuivre. Un anneau se met en place autour d'un axe, porteur de différents acides aminés alignés et positionnés sur différents sites. C'est alors qu'un bras moléculaire vient se fixer à l'anneau. En glissant le long de l'axe, il rencontre les unités peptidiques qui obstruent le passage. Le bras les enfile alors les unes après les autres pour former une protéine qui est achevée et devient disponible une fois que l'anneau est passé sur tous les sites.
Une machine très loin d’égaler les ribosomes
Cependant, il faut faire preuve de patience et surtout ne pas espérer construire des molécules complexes. Là où une seconde suffit à un ribosome pour assembler 20 acides aminés, il faut 12 heures au nanorobot pour en mettre quatre bout à bout. De plus, à la différence de l'organite cellulaire qui laisse le code génétique intact et permet une deuxième puis une troisième lecture (jusqu'à ce que l'ARN se dégrade), un même axe ne peut fournir qu'un seul peptide.
C'est pourquoi les auteurs ont eu recours à environ 1018 (un milliard de milliards) de ces nanorobots travaillant en parallèle pour obtenir quelques milligrammes de courtes protéines avec une séquence unique. L'idée à terme est de produire des molécules en massemasse. Mais des améliorations s'avèrent nécessaires pour synthétiser des protéines bien plus imposantes. C'est l'objectif après lequel courent les chercheurs.